UPD Chemists nag-develop ng AI Tool Laban sa Drug-Resistant Bacteria
Published: May 12, 2026
By: Eunice Jean C. Patron
Translated by: Dr. Eizadora T. Yu
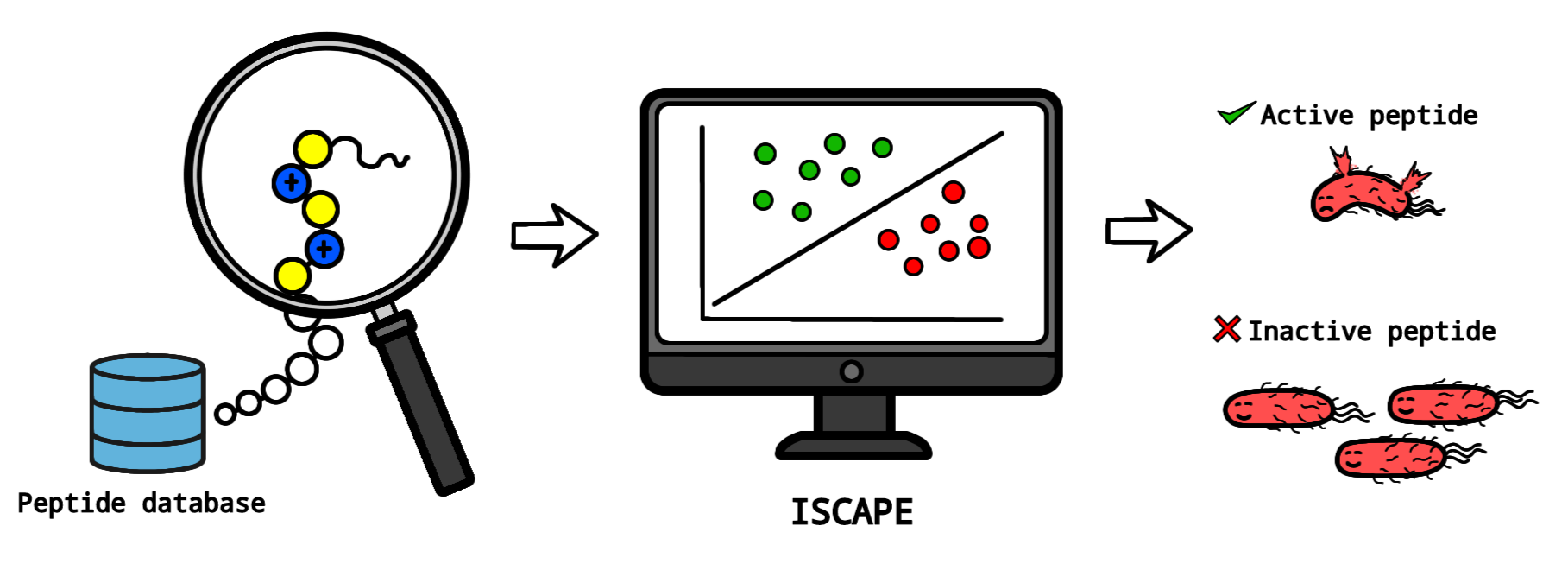
Habang patuloy ang paghina o pagkawalang bisa ng mga tradisyunal na antibiotic sanhi ng antimicrobial resistance (AMR), ay lalong nagiging mahalaga ang paghahanap ng mga bagong gamot. Isa sa mga pinakapromising na solusyon ay ang antimicrobial peptides (AMPs), na isang klase ng mga compound na kayang pumatay ng bacteria. Upang mapabilis ang proseso ng pagtuklas ng AMPs, bumuo sila Remmer Salas, Dr. Portia Mahal Sabido, at Dr. Ricky Nellas ng University of the Philippines Diliman – College of Science (UPD-CS) ng isang AI tool.
Ang ISCAPE (Interpretable Support Vector Classifier of Antibacterial Activity of Peptides against Escherichia coli) ay isang AI-powered tool na tumutulong na mag-predict kung ang isang peptide ay may kakayahang pumatay o pumigil sa pagdami ng E. coli. Kailangan lamang ng system na ito ng Simplified Molecular-Input Line-Entry System (SMILES) string bilang input, bagay na magpapadali sa mga researcher na suriin ang mga kandidatong molecule.
“Ayon sa tradisyunal na paraan, ang pagtuklas ng antibacterial peptides ay nangangailangan ng paggawa o pag-synthesize ng maraming kandidato at pagsubok sa mga ito isa-isa. Matagal ang prosesong ito,” sabi ni Salas. “Gumamit kami ng AI upang matuto mula sa umiiral na datos at matukoy ang mga pattern na nagkakaiba sa mga aktibo at hindi aktibong peptide.”
Bukod-tangi din sa mga AI tools ang abilidad ng ISCAPE na tukuyin kung aling mga molecular feature ang nagpapabisa sa isang peptide. Ayon kay Salas, nakatutulong ito upang makatipid ng oras at resources ang mga researcher. Nababawasan nito ang trial-and-error experiments at nagbibigay-daan upang mas mahusay na makapagdisenyo ng peptide.
“Tumutulong ang ISCAPE sa laban sa antimicrobial resistance sa pamamagitan ng pagpapabilis ng early-stage screening gamit ang data-driven peptide design,” dagdag pa ni Salas. “Hindi nito pinapalitan ang laboratory experiments, ngunit ginagawa nitong mas episyente ang discovery process at tinutulungan ang mga researcher na magpokus sa mga pinakapromising na kandidato.”
Maaaring ding magamit ang AI-powered model laban sa ibang bacteria bukod sa E. coli. Gayunpaman, kailangan muna itong sanayin muli gamit ang mataas na kalidad na datasets na partikular sa bacterial strains na nais pag-aralan. Maaari ring gamitin ang ISCAPE approach upang hulaan o mag-predict ng activity ng iba pang bioactive peptides.
“Ang paggamit ng ISCAPE para sa ibang biological targets ay nangangailangan ng maayos na curated datasets na may experimentally validated activity,” dagdag ni Salas. “Pagkatapos nito, kailangang sanayin muli ang model gamit ang molecular features na natukoy naming pinakamainam para sa peptides.”
Umaasa ang grupo na makatutulong ang ISCAPE upang mas mahusay at mas mabilis na makapagdisenyo ang mga researcher ng antibacterial peptides at makatulong sa pandaigdigang laban kontra AMR.
Bukas sa publiko ang ISCAPE para magamit ng ibang siyentista. Maaaring ma-access ang web server nito sa Hugging Face Spaces. Available din sa GitHub ang training data at code para sa large-scale prediction.
Ang research paper na pinamagatang “Interpretable support vector classifier for reliable prediction of antibacterial activity of modified peptides against Escherichia coli” ay nailathala sa Journal of Molecular Graphics and Modelling. Ang internasyonal na publikasyong ito ay naglalaman ng mga papel tungkol sa paggamit ng computer sa teoretikal na pag-aaral ng molecular structure, function, interaction, at design. Saklaw nito ang lahat ng aspeto ng molecular modeling at computational chemistry.
References:
Salas, R. L., Sabido, P. M., & Nellas, R. B. (2026). Interpretable support vector classifier for reliable prediction of antibacterial activity of modified peptides against Escherichia coli. Journal of Molecular Graphics and Modelling, 142, 109188. https://doi.org/10.1016/j.jmgm.2025.109188
For interview requests and other concerns, please contact media@science.upd.edu.ph.
